4次元細胞データによる細胞移動の論文たち
(3次元+時間)の4次元データを取り扱うための情報収集兼イメージ作り。以下の論文たちは乱読したもので正確なレビューではないことに注意。引用された文献やsupplementの情報から画像処理の方法やアルゴリズムは別にまとめる予定。
1. 光シート顕微鏡を使ったゼブラフィッシュの発生中のsingle-cellデータ分析
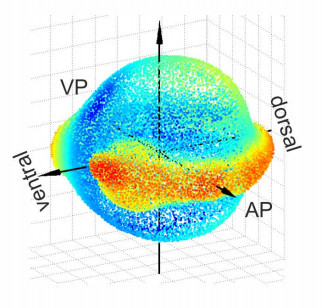
光シート顕微鏡を使って1細胞解像度で16hpf(hours postfertilization)までデータを収集したものを分析したという論文。立体的な構造がよく分かる。azimuthが経度、altitudeが緯度を表し、上下が対象になるような座標系を胚に対して設定する。右下の図はwikipediaより。
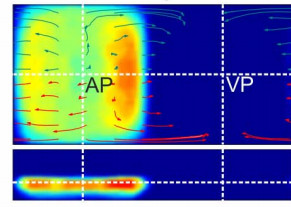
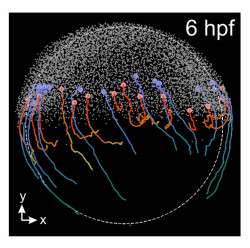
未処理だと~1TB/hのデータが発生するらしく、実際には3次元の極座標系でセルに分割してそこでの個数の変化を「ベクトル場」として観測している。下のグラフは球面をGall-Peters Projectionで写したもので面積が保存されていて、密度を表すのに適している。APが動物極でVPが植物極を表す。細胞が流れる様子が分かる。右下図はこの実験とは別だが細胞の移動経路も撮影されていて、これは分割されたセルから計算できる「流れ」と概ね一致する。赤がhypoblast(胚盤葉下層)、青がepiblast(胚盤葉上層)。
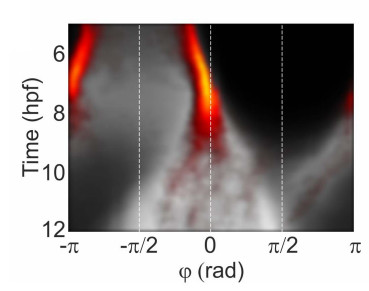
時系列データの表示方法としては、kymograph(角度記録方法の1つの名前?)が使われている。色は細胞密度を表す。
2. 多光子顕微鏡を使ったショウジョウバエの原腸形成の細胞移動分析
Quantitative imaging of collective cell migration during : Drosophila: gastrulation: multiphoton microscopy and computational analysis : Abstract : Nature Protocols http://www.ncbi.nlm.nih.gov/pmc/articles/PMC2854020/
ショウジョウバエの原腸形成の際の細胞移動を4Dで撮影して分析しようという上の論文と同じような記事。こちらはmatlabスクリプトとデータを公開している。